03.09.2018 Wasser macht Platz für Komplexbildung von Proteinen
Europäische Forschergruppe analysiert Wasserstruktur in einem Protein
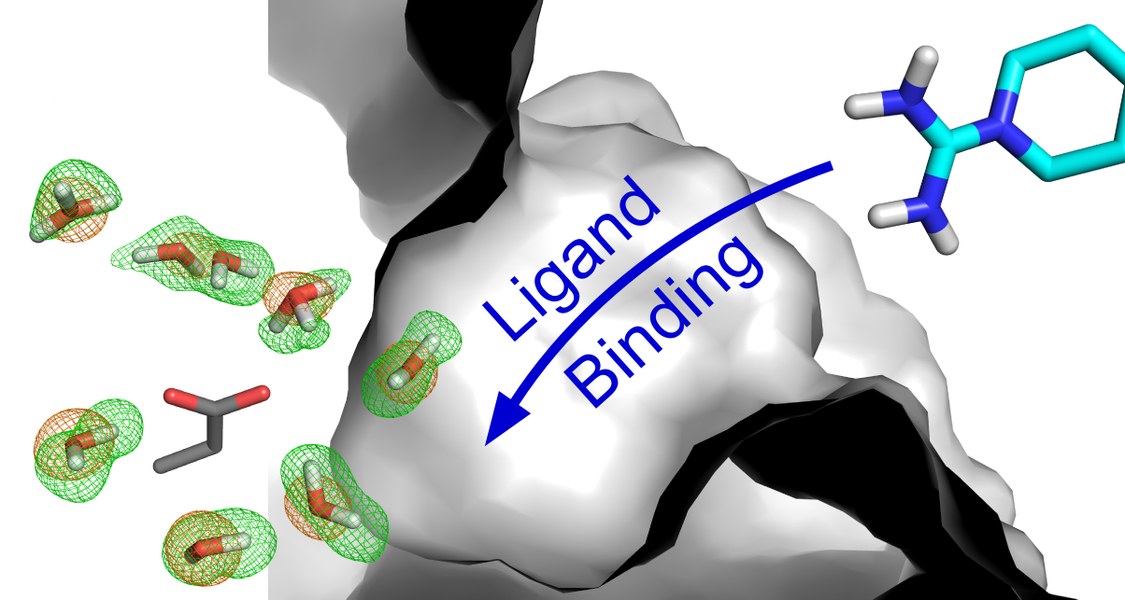
Wasser marsch! Bevor Proteine sich mit Bindungspartnern zusammenschließen, füllen Wassermoleküle den Hohlraum, den die Proteine für ihre Bindungspartner bereithalten. Das hat eine europäische Forschergruppe um den Marburger Chemiker Professor Dr. Gerhard Klebe experimentell untersucht, indem sie die Lage des Wassers in einem Protein mit ausgeklügelten Methoden analysierte. Die Wassermoleküle lassen sich aufgrund ihrer großen Beweglichkeit mehr oder weniger leicht entfernen, um den Bindungspartnern Platz zu machen. Die Wissenschaftler berichten in der aktuellen Ausgabe des Magazins „Nature Communications“ über ihre Ergebnisse.
Proteine und andere Biomoleküle sind in der Zelle von Wassermolekülen umgeben. „Solange wir nicht wissen, wo sich Wassermoleküle befinden und wie sich ihre Lage verändert, bleiben unsere Erkenntnisse über die Wechselwirkung zwischen Proteinen und ihren Bindungspartner lückenhaft“, erklärt Gerhard Klebe, der die Studie leitete.
„Nahezu jeder biologische Prozess verläuft über die wechselseitige Erkennung, Bindung und oft auch chemische Umsetzung von Biomolekülen“, führt der Pharmazeut aus: „Substrate, Hormone und andere Signalstoffe, aber auch Arzneimittel binden an Proteine, um dadurch ihre spezifische Wirkung zu erzielen.“ Bei der Wechselwirkung bilden sich insbesondere Wasserstoffbrücken zwischen den Bindungspartnern aus.
Wasser beeinflusst massiv die Wechselwirkung, die Proteine mit ihren Reaktionspartnern eingehen. Dieser Umstand ist auch für Arzneimittel von Belang. Ein Beispiel bietet das Enzym Thrombin, das an der Blutgerinnung beteiligt ist: Das Bindungsverhalten von Thrombin ändert sich dramatisch, wenn einzelne Wassermoleküle aus seiner Bindungstasche entfernt werden. Diese Entdeckung hat zu verbesserten Gerinnungshemmern geführt.
„Trotz dieser Bedeutung von Wassermolekülen für die Bindung sind experimentelle und insbesondere strukturelle Daten leider selten, die das Verhalten von Wassermolekülen während der Komplexbildung zwischen Protein und Bindungspartner erklären“, beklagt Klebe. Diese Lücke schließt sein Team nun durch Strukturanalysen, für die es sich der Neutronendiffraktions-Methode bediente. Diese beruht auf der Bestrahlung der Proteinkristalle mit Neutronen, deren Streuung die Proteinstruktur widerspiegelt. „Zwar sind bislang an die 150.000 Proteinstrukturen aufgeklärt worden, meist mit Röntgenstrahlung“, gibt der Pharmazeut zu bedenken; aber durch deren geringe Streukraft sei der Wasserstoff in den Strukturen in aller Regel nicht erkennbar. Hier kann die Neutronenkristallographie helfen, da sie Wasserstoffe sehr gut sichtbar macht. „Die Zahl an Neutronenstrukturen fällt jedoch sehr, sehr gering aus“, legt Klebe dar: „Sie liegt bei unter 0,1 Prozent.“
Das Forscherteam untersuchte das Verdauungsenzym Trypsin, das zu einer Proteinfamilie gehört, deren Mitglieder für zahlreiche Krankheiten verantwortlich gemacht werden. „Unsere Studie liefert die am besten aufgelösten Neutronenstrukturen, die bisher an Proteinen dieser Größe durchgeführt wurden“, betont Klebe. Die Neutronendiffraktions-Daten kombinierten die Forscher mit hochauflösenden Röntgenaufnahmen sowie mit biochemischen und biophysikalischen Messungen.
Die Daten beschreiben sehr präzise, wo sich Wasserstoffatome vor und nach der Anlagerung eines Bindungspartners befinden und wie sich das Muster ändert. Vor der Bindung wird die Bindungstasche mit Wassermolekülen besetzt, die eher schlecht durch Wasserstoffbrücken vernetzt sind, so dass sie sich teilweise durch eine hohe Mobilität auszeichnen. „Dies ist wahrscheinlich ein Schlüsselfaktor, der die Verdrängung des Wassers und dadurch die Anlagerung von Bindungspartnern fördert“, schreiben die Autoren. „Der Unterschied zwischen vorher und nachher gibt einen Eindruck davon, welche Wasserstoffbrücken gebrochen werden müssen, um die Komplexbildung zu ermöglichen.“
„Solch eine detaillierte Beschreibung ist von entscheidender Bedeutung, um zu verstehen, wie die Bindung vonstattengeht“, hebt Klebe hervor. „Wir sind überzeugt, dass die gewonnenen Erkenntnisse für ein breites Spektrum vergleichbarer Komplexe gelten.“
Professor Dr. Gerhard Klebe lehrt Pharmazeutische Chemie an der Philipps-Universität Marburg. Für seine Forschungsarbeit erhielt er im Jahr 2011 einen „ERC Advanced Grant“ des Europäischen Forschungsrates. Durch diese Fördermaßnahme gewannen Klebe und seine Arbeitsgruppe entscheidende Einblicke in das Bindungsverhalten von Arzneistoffen an Proteine; das Team legte die gewonnen Erkenntnisse in etwa 30 Publikationen dar, die den zuvor deutlich unterschätzten Einfluss von Wasser auf die Arzneistoffbindung in facettenreicher Weise verdeutlichen.
Koautor Dr. Johannes Schiebel ist Träger des Promotionspreises 2015 der Gesellschaft Deutscher Chemiker. Die vorliegende Studie wurde zusätzlich durch ein Kurzzeitstipendium der Europäischen Organisation für Molekularbiologie an Johannes Schiebel finanziell gefördert.
Originalveröffentlichung: Johannes Schiebel & al.: Intriguing role of water in protein-ligand binding studied by neutron crystallography on trypsin complexes, Nature Communications 2018, DOI: 10.1038/s41467-018-05769-2
Literatur: Gerhard Klebe: Wirkstoffdesign. Entwurf und Wirkung von Arzneistoffen, Heidelberg (Springer) 2009, ISBN 978-3-8274-2046-6, 637 Seiten
Pressemitteilung zum ERC-Grant